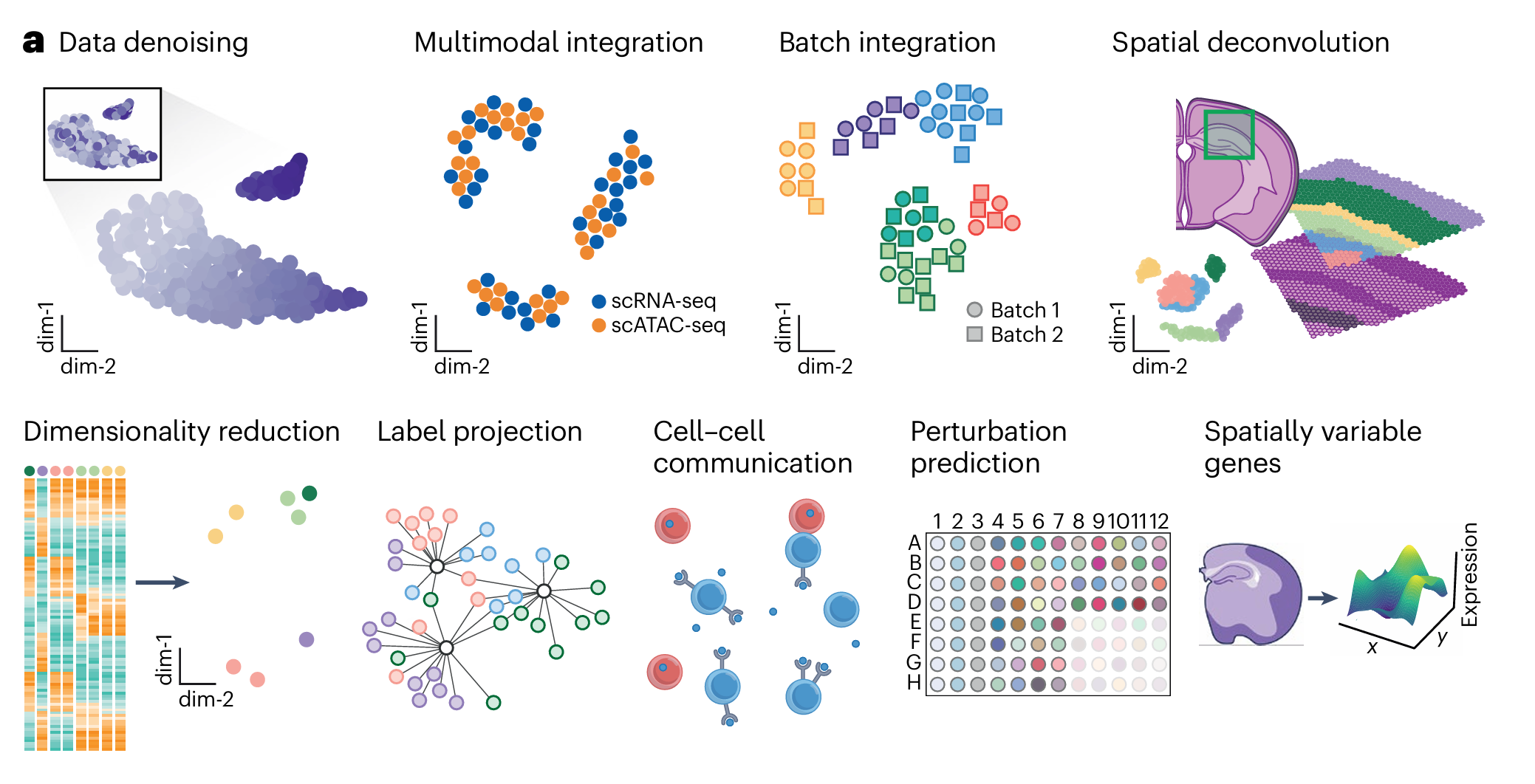
单细胞算法典型任务
发表于|更新于|Paper Reading
|总字数:7|阅读时长:1分钟|浏览量:
📖 论文阅读记录
TASK
文章作者: 鱼幼薇
版权声明: 本博客所有文章除特别声明外,均采用 CC BY-NC-SA 4.0 许可协议。转载请注明来源 小鱼日记!
相关推荐
2025-09-25
Bering
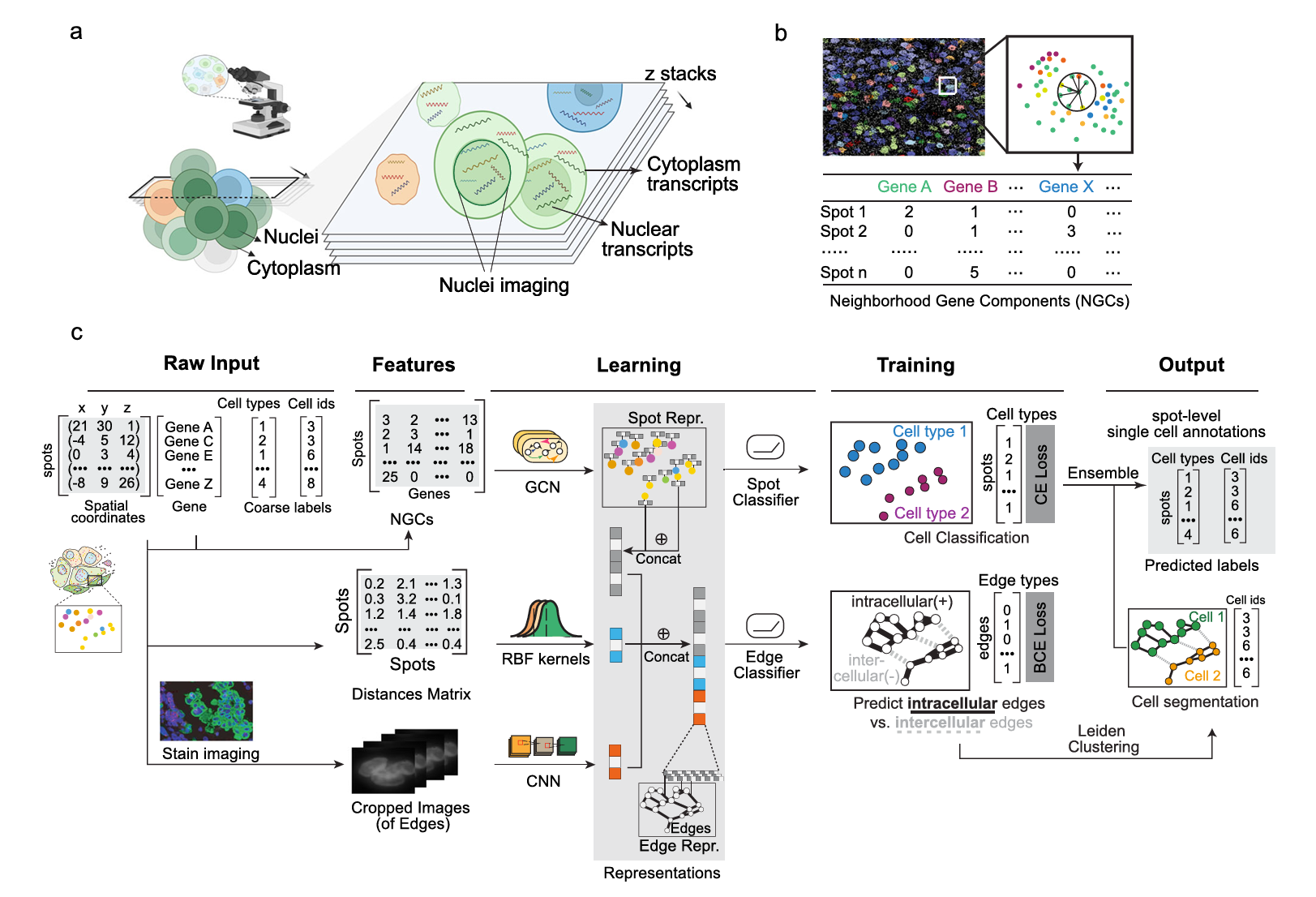
论文阅读记录Bering 标题:Bering: joint cell segmentation and annotation for spatial transcriptomics with transferred graph embeddings 作者:Harvard University 发表会议/期刊:Nature Communications 年份:2025 链接:Bering 主要内容简介 Motivation:Some tissues have densely packed cells with unclear boundaries, making it difficult to perform accurate segmentation Task:Cell segmentation and annotation for spatial transcriptomics 方法与创新点 总体框架: 方法概述: 图构建,NGC 图卷积和全连接网络 节点分类 边嵌入由三部分组成- node representation-...
2025-09-08
Deep Fusion Clustering Network
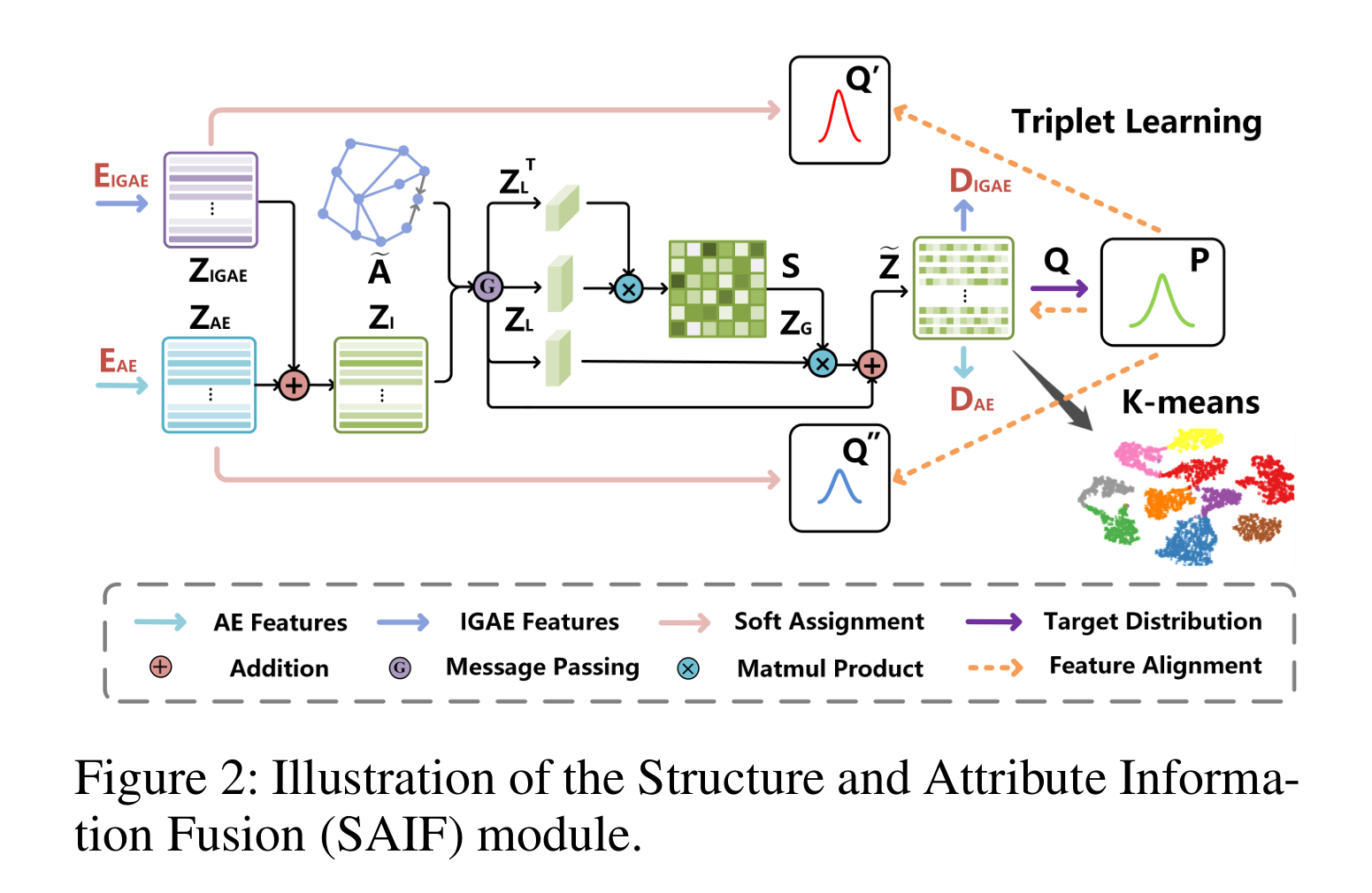
📖 论文阅读记录1. 基本信息 论文题目:Deep Fusion Clustering Network 作者/机构:National University of Defense Technology 会议/期刊:AAAI 年份:2021 2. 研究背景 研究领域:深度聚类 主要问题: 缺乏动态融合机制来选择性整合和精炼图结构与节点属性的信息以达成共识表示学习; 未能从双方提取信息以生成鲁棒的目标分布(即“真实”软标签)。 相关工作: 属性图聚类 目标分布生成 3. 核心贡献 ✨ 创新点:通过SAIF模块实现AE与IGAE的特征深度融合 4. 方法 SAIF总体框架: 标号: Fusion-based Autoencoders Structure and Attribute Information Fusion Joint loss and Optimization 5. 实验 数据集: ...
2025-09-21
GraphST
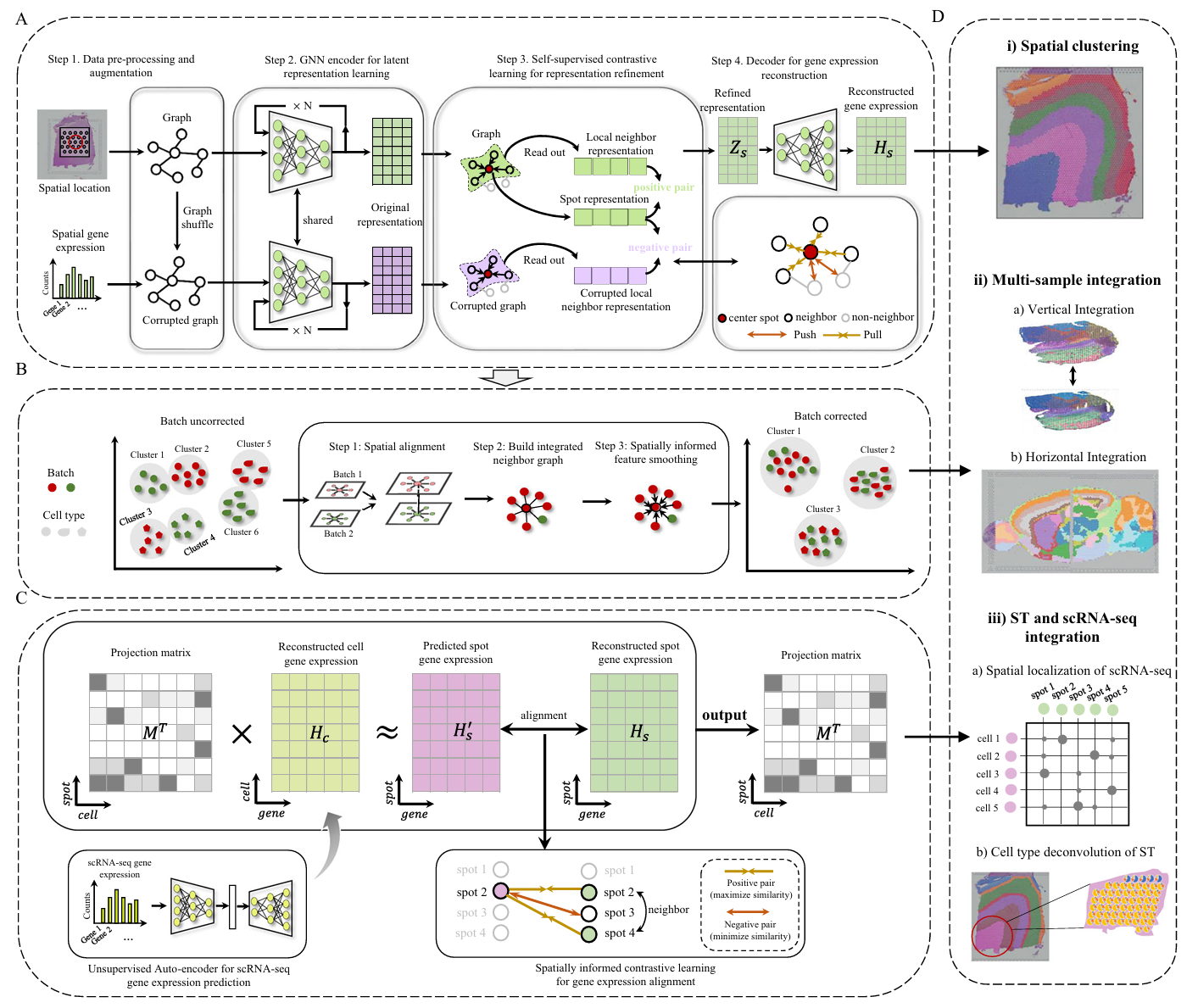
论文阅读记录GraphST 标题:Spatially informed clustering, integration,and deconvolution of spatial transcriptomics with GraphST 作者:National University of Singapore (NUS) 发表会议/期刊:Nature Communications 年份:2023 链接:GraphST 主要内容简介 Motivation: 反卷积未利用空间信息 多样本整合未利用空间信息 方法与创新点 总体框架: 方法概述: graph self-supervised contrastive learning framework: data augmentation GNN-based encoder for representation learning self-supervised contrastive learning for representation refinement ...
2025-09-21
DeepST
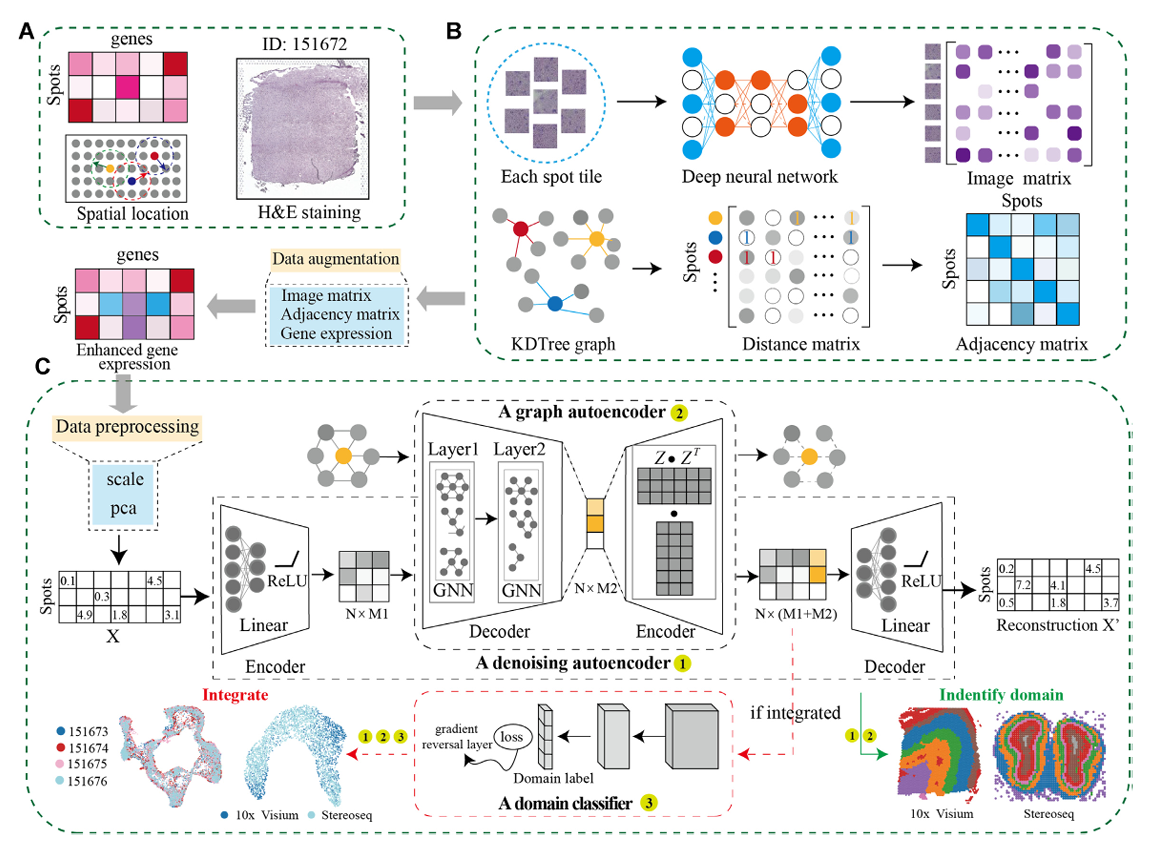
论文阅读记录DeepST 标题:DeepST: identifying spatial domains in spatial transcriptomics by deep learning 作者:Harbin Institute of Technology 发表会议/期刊:Nucleic Acids Research 年份:2022 链接:DeepST 主要内容简介 Motivation: 先前方法主要依赖线性主成分分析来提取基因表达的高变特征,因此无法建模复杂的非线性相互作用 未充分利用空间信息,且在预测组织结构方面存在局限 大多数分析大量ST数据的空间方法无法正确校正批次效应,且不能处理其他空间组学数据,使其通用性不足 方法与创新点 总体框架: 方法概述: Spatial data...
2025-09-23
IE-HERCL
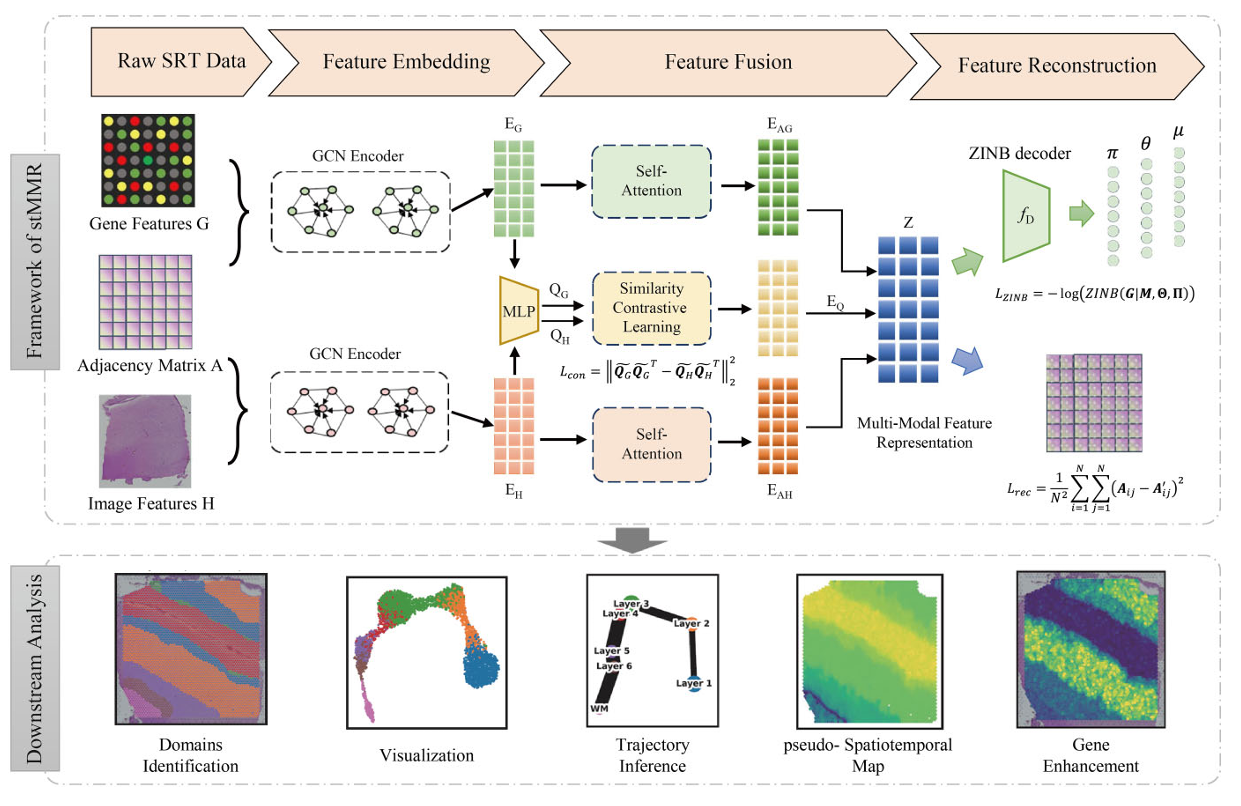
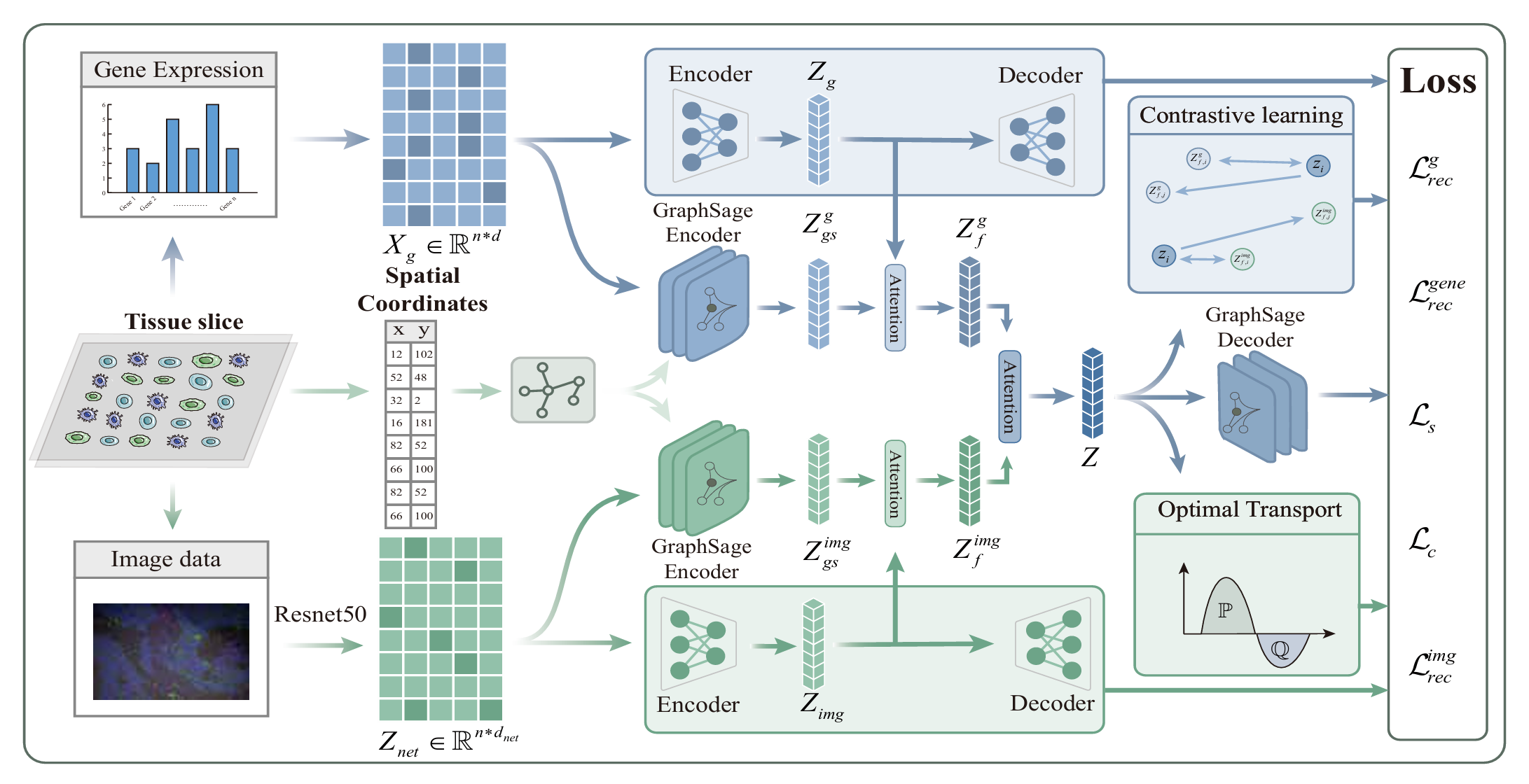
论文阅读记录IE-HERCL 标题:Image-Enhanced Hybrid Encoding with Reinforced Contrastive Learning for Spatial Domain Identification in Spatial Transcriptomics 作者:Central South University 发表会议/期刊:IJCAI 年份:2025 链接:IE-HERCL 主要内容简介 Motivation: Exisisting methods fail to account for complex interdependencies between modalities. 方法与创新点 总体框架: 方法概述: Multimodal Feature Representation Learning utilize AE to extract & Loss function L_rec: $$L^g_{rec} = | X_{g,i} -...
2025-09-11
基于代码理解MAFN
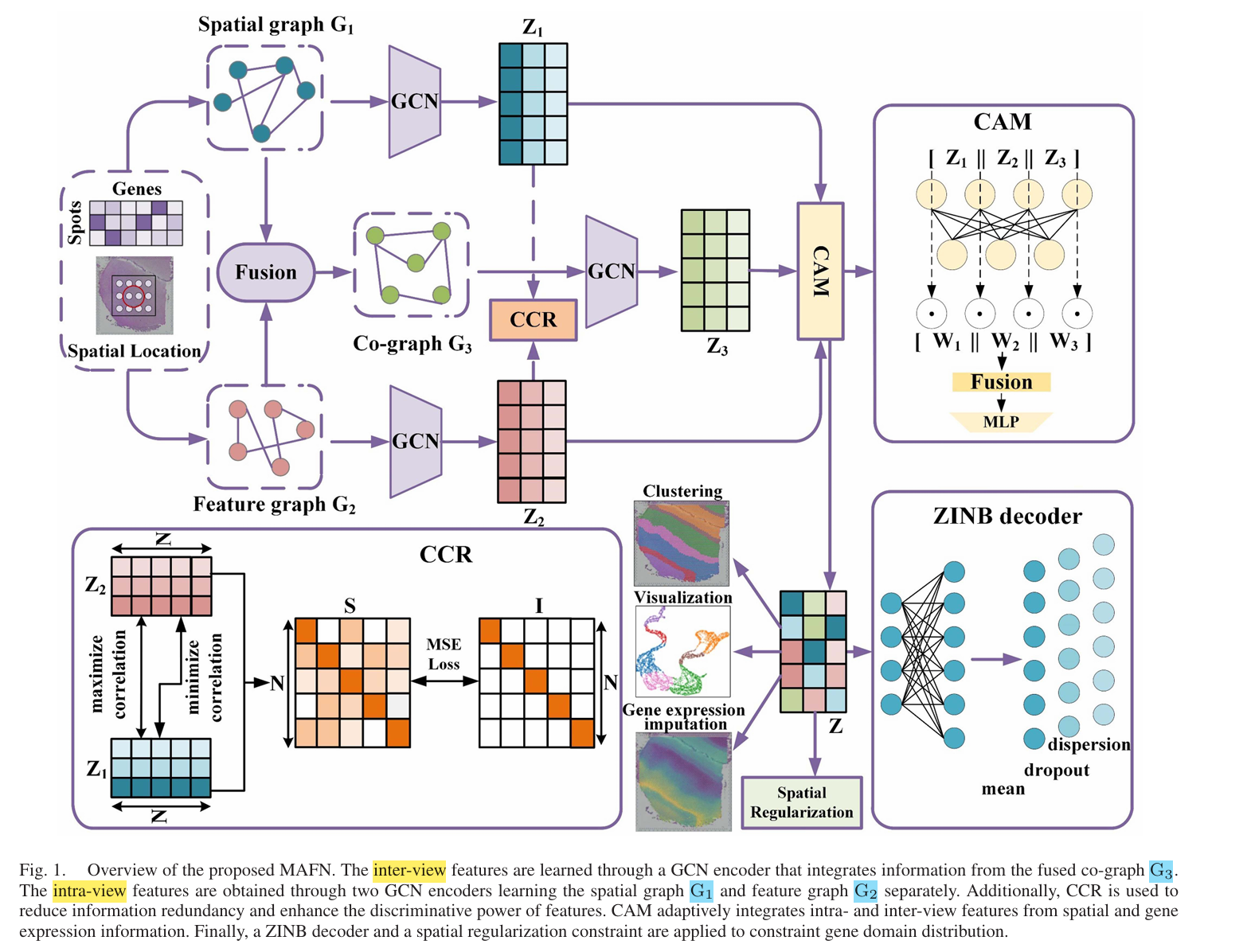
论文阅读记录1. 基本信息 论文题目:Multi-View Adaptive Fusion Network for Spatially Resolved Transcriptomics Data Clustering 作者/机构:China University of Geosciences 会议/期刊:IEEE TRANSACTIONS 年份:DECEMBER 2024 论文链接:MAFN_IEEE 2. 方法总览 总体框架: 关键技术路线: spatial graph G1(euclidean distance & r), feature graph G2(cosine similarity & kNN) Inter-View Complementary Features Learning (GCN) Intra-View Discriminative Features Learning(GCN + Lc –> (S-I)^2) Cross-View Attention Module (CAM) Gene...